Sentieon
Sentieon 中文手册
Sentieon 中文手册(上册)
Sentieon 中文手册(下册)
Sentieon 软件应用教程
Sentieon | 联合Dell、AMD开发基因组大数据分析加速方案
Sentieon | 应用教程: 利用Sentieon Python API引擎为自研算法加速
Sentieon | 应用教程: 关于读段组的建议
Sentieon | 应用教程: 使用DNAscope对HiFi长读长数据进行胚系变异检测分析
Sentieon | 应用教程: TNscope® 使用机器学习模型进行有匹配正常样本的体细胞变异发现
Sentieon | 应用教程: CCDG使用Sentieon®的功能等效流程
Sentieon | 应用教程: 利用共识功能去除PCR重复
Sentieon | 应用教程: 适用于PacBio HiFi和Oxford Nanopore长读长测序数据的结构变异检测
Sentieon | 应用教程: 使用 Sentieon进行大型基因组重测序分析
Sentieon | 应用教程: 体细胞SNP/Indel变异检测
Sentieon | 应用教程: DNAscope使用机器学习模型进行胚系变异调用
Sentieon | 应用教程: 唯一分子标识符(UMI)
Sentieon | 应用教程: Sentieon分布模式
Sentieon | 应用教程:使用CNVscope进行CNV检测分析
Sentieon发布核心家系(trio)基因分析最佳实践方案
Sentieon推出Segdup-caller:针对片段重复区域的专用精准变异检测工具
Sentieon-cli | DNAscope WES 流程单条命令版本详解
Sentieon | DNAscope 核心家系(trio) WES 分析全流程详解
Sentieon | DNAscope Hybrid长短读长混合分析流程详解及评测
Sentieon | 基于Illumina WGS数据的高精度、低成本的泛基因组分析方案
Sentieon软件版本更新
Sentieon | 发布V202503.01版本
Sentieon | 发布V202503.02版本
Sentieon | 发布V202503.03版本
Sentieon软件快速入门指南
Sentieon 软件模块总述
Sentieon 特色流程 - DNAscope
Sentieon | DNAscope Illumina 流程
sentieon | DNAscope Complete Genomics 流程
Sentieon | DNAscope LongRead PacBio 流程
Sentieon | DNAscope Ultima Genomics 流程
Sentieon | DNAscope Element Bio 流程
Sentieon | DNAscope LongRead Nanopore 流程
Sentieon混合分析流程 - DNAscope Hybrid
Sentieon推出混合型短读长和长读长变异检测DNAscope Hybrid流程(上)
Sentieon推出混合型短读长和长读长变异检测DNAscope Hybrid流程(下)
毅硕Sentieon | 泛基因组分析流程详解
毅硕Sentieon | RNA-seq 变异检测全流程详解
毅硕Sentieon | 物种全基因组(WGS)分析流程
毅硕Sentieon | 植物全基因组(WGS)分析流程
毅硕Sentieon | 小麦(Triticum aestivum)全基因组WGS分析流程
毅硕Sentieon | 水稻(Oryza sativa)全基因组WGS分析流程
毅硕Sentieon | 拟南芥(Arabidopsis thaliana)全基因组WGS分析流程
毅硕Sentieon | 马铃薯(Solanum tuberosum)全基因组WGS分析流程
毅硕Sentieon | 巨桉(Eucalyptus grandis)全基因组WGS分析流程
毅硕Sentieon | 向日葵(Helianthus annuus)全基因组WGS分析流程
毅硕Sentieon | 野草莓(Fragaria vesca)全基因组WGS分析流程
毅硕Sentieon | 银杏(Ginkgo biloba)全基因组WGS分析流程
毅硕Sentieon | 大豆(Glycine max)全基因组WGS分析流程
毅硕Sentieon | 陆地棉(Gossypium hirsutum)全基因组WGS分析流程
毅硕Sentieon | 胡桃(Juglans regia)全基因组WGS分析流程
毅硕Sentieon | 苹果(Malus domestica)全基因组WGS分析流程
毅硕Sentieon | 动物全基因组(WGS)分析流程
毅硕Sentieon | 猪(sus scrofa)全基因组WGS分析流程
毅硕Sentieon | 鸡(Gallus gallus)全基因组WGS分析流程
毅硕Sentieon | 家鼠(Mus musculus)全基因组WGS分析流程
毅硕Sentieon | 家犬(canis lupus familiaris)全基因组WGS分析流程
毅硕Sentieon | 东方蜜蜂(Apis cerana)全基因组WGS分析流程
毅硕Sentieon | 电鳗(Electrophorus electricus)全基因组WGS分析流程
毅硕Sentieon | 红隼(Falco tinnunculus)全基因组WGS分析流程
毅硕Sentieon | 家猫(Felis catus)全基因组WGS分析流程
毅硕Sentieon | 尼罗罗非鱼(Oreochromis niloticus)全基因组WGS分析流程
毅硕Sentieon | 狮子(Panthera leo)全基因组WGS分析流程
毅硕Sentieon | 东北虎(panthera tigris altaica)全基因组WGS分析流程
毅硕Sentieon | 黑猩猩(pan troglodytes)全基因组WGS分析流程
毅硕Sentieon文献解读
Sentieon文献解读 | Population Sequencing
Sentieon文献解读 | Agrigenomics
Sentieon | Agrigenomics-泛基因组揭示小麦结构变异与栖息地及育种的关联
Sentieon文献解读 | Genetic Disease
Sentieon文献解读 | Tumor Sequencing
Sentieon文献解读 | Benchmark and Method Study
Sentieon文献解读 | Long Read Sequencing
Sentieon文献解读 | Clinical Trial
Sentieon文献解读 | Epidemiology
Sentieon文献解读 | Gene Editing
Sentieon文献解读 | Liquid Biopsy
Sentieon | TNscope 分析流程详解
-
+
首页
Sentieon | 联合Dell、AMD开发基因组大数据分析加速方案
# 一、背景 随着生物医学研究全面进入“大组学”时代,人类全基因组测序(30x WGS)的成本已降至千元以下,测序效率的飞跃导致数据量呈指数级增长,使下游分析遭遇了严峻的算力瓶颈。传统的生信分析框架往往面临运行效率低、硬件资源利用率不足的问题。为此,Sentieon、Dell Technologies 与 AMD 的三方强强联手,证明了在通用多核 CPU 上运行高度优化的软件,是当前应对复杂变异检测、平衡灵活性与经济性的最优解决方案。 本文将通过详实的基准测试数据,展示基于第五代 AMD EPYC 处理器的 Dell PowerEdge 服务器在处理多元化序列数据集时 Sentieon 所展示的卓越性能。 * * * # 二、测试服务器配置 本次测试构建了包含标准数据集、前沿硬件及最新算法模型的测试矩阵。以下是详细的配置: ## 1. 基准测试数据集 本次基准测试使用 Fastq 格式的 GIAB HG002 样本。 * 短读长数据:采用 Illumina NovaSeq 平台数据;其中单样本被降采样至 30X 覆盖度,同时引入未经降采样的多样本数据集。 * 长读长数据:采用 PacBio Sequel II (HiFi) 降采样至 30X 覆盖度的数据,以及来自人类泛基因组参考联盟的 Oxford Nanopore (ONT) 覆盖度为 29.6X 的数据。 ## 2. 本地及云端的硬件配置 * 在本地部署中,采用了两台配备了双 1.92TB NVMe 数据盘、镜像 NVMe 启动盘以及 1,536GB 超大内存的Dell PowerEdge R7725 服务器。一台搭载了双路 AMD EPYC 9755 处理器,单颗 128 核心,2.7GHz;另一台则搭载了双路 AMD EPYC 9965 处理器,单颗 192 核心,2.2GHz,利用超高核心数释放多样本并行处理优势。 * 在云端部署中,选用 Amazon EC2 Hpc7a 实例,配合高速 gp3 EBS 存储。而为了消除云端磁盘 I/O 瓶颈,测试中使用了内存盘缓存中间文件,能释放出 Sentieon 软件的极致性能。同时在 Oracle Cloud 部署了 BM.GPU.H100.8 机型,通过 8x NVIDIA H100 GPU 以及配套的集群网络,作为 Sentieon CPU 优化方案的性能对标基准。 ## 3. 本地及云端的软件配置 测试全程基于 Sentieon V202503.01 版本。并针对不同平台,精准匹配了 DNAscope 机器学习模型包(Illumina WGS 使用v2.2、PacBio HiFi 使用 v2.1 及 ONT使用 v2.1模型),确保在极速分析的同时保障变异检测的灵敏度与特异性。 * * * # 三、加速方案性能优势 ## 1. 二代短读长单样本性能评估 使用搭载 AMD EPYC 9755 处理器的 Dell PowerEdge R7725 服务器,Sentieon 软件处理 30x Illumina NovaSeq 全基因组样本总耗时 9.5 分钟;而在搭载 AMD EPYC 9965 处理器的 Dell PowerEdge R7725 上总耗时为 10.0 分钟。比在 8x NVIDIA H100 GPU 上快约 28%,且比使用上一代 CPU (hpc 7a.96xlarge)的基准测试快约 18%。 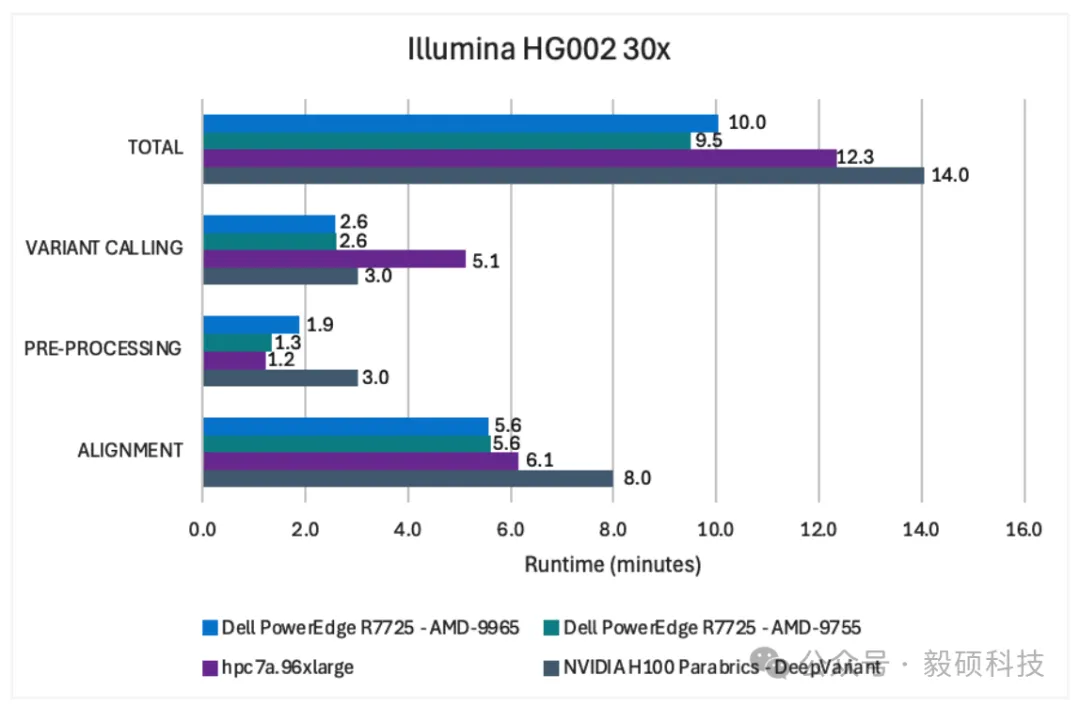 图1 Sentieon DNAscope 与 NVIDIA 运行性能表现 上图直观地展示出 Sentieon DNAscope 流程在本地及云端部署的运行性能优于 NVIDIA Parabricks。而这卓越的性能优势得益于硬件架构与软件算法的共同优化。 ## 2. 三代长读长单样本性能评估 在使用 Amazon EC2 hpc7a.96xlarge 实例进行的基准测试中,Sentieon 使用 DNAscope LongRead 流程处理了覆盖度约为 30x 的 PacBio HiFi 和 Oxford Nanopore Technologies (ONT) duplex 测序数据集。 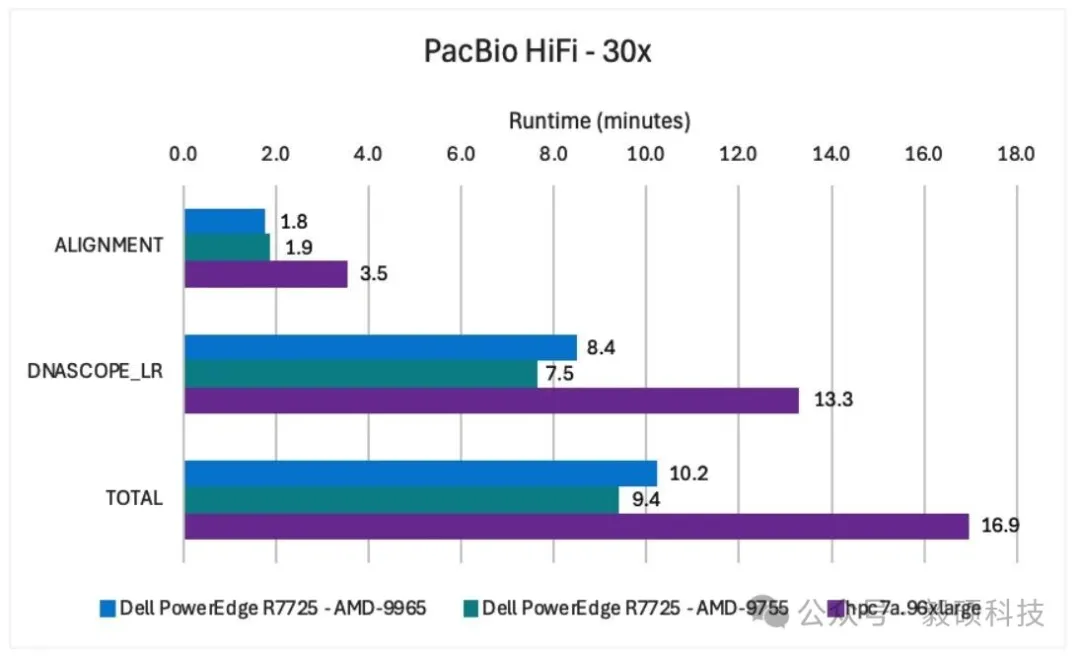 图2 Sentieon DNAscope LongRead 在 PacBio HiFi 数据上的性能表现 结果显示,使用搭载两套不同处理器的 Dell PowerEdge R7725 服务器对 30X PacBio HiFi 样本的处理总耗时均在 10.2 分钟内,而在 hpc7a.96xlarge 实例上总耗时为 16.9 分钟。 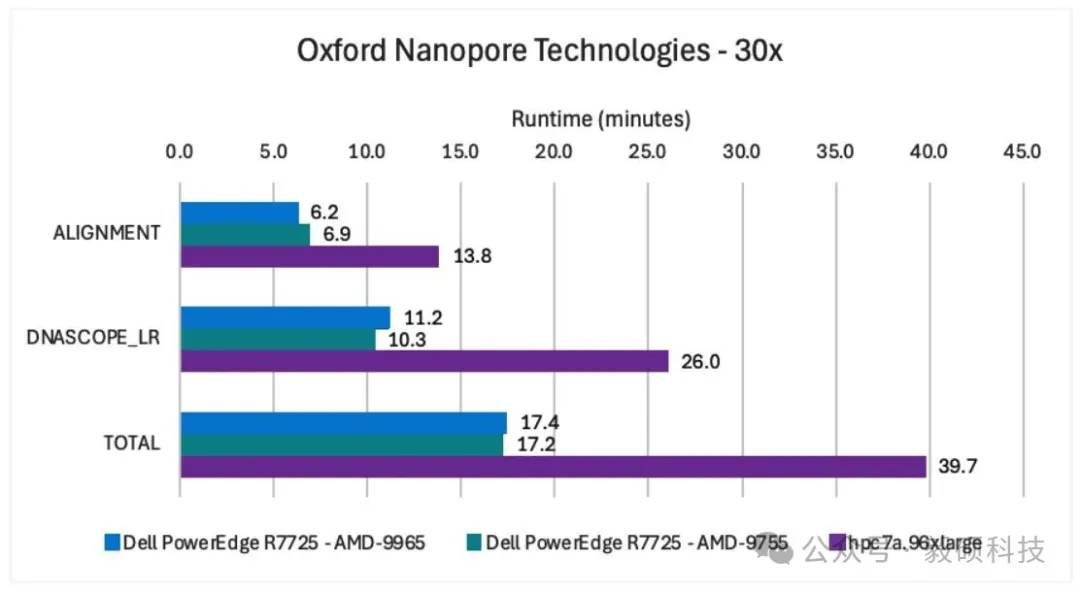 图3 Sentieon DNAscope LongRead 在 ONT 数据上的性能表现 在处理包含大量复杂结构变异信息的 ONT 样本时,两套不同配置的 Dell PowerEdge R7725 均展现了卓越的计算效率,其总耗时均被压缩至 17.4 分钟以内;而在 hpc7a.96xlarge 实例总耗时为 39.7 分钟。 本次测试运行时间的压缩是硬件和软件共同改进的结果。这种跨代级的性能提升,显著缓解了三代测序在临床应用中“测序快、分析慢”的痛点。 # 3. 多样本并发处理能力与吞吐量评估 为评估流程在大规模工作负载时的表现,Sentieon 在单台服务器上同时并行处理了 8 个 Illumina NovaSeq 30x 样本。 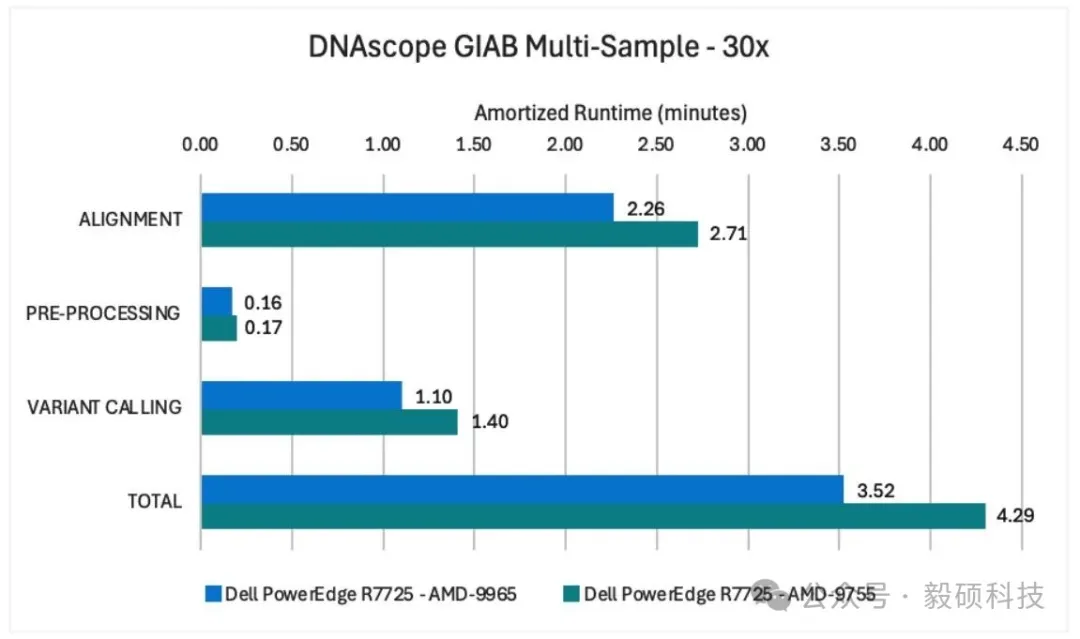 图4 Sentieon DNAscope 在多样本处理中的性能表现 在多样本并发测试中,Sentieon 展现了卓越的资源调度能力。Sentieon 在处理这 8 个 30x 样本的均摊单样本总耗时不到 4.29 分钟,所有样本在两台服务器上的总耗时均在 40 分钟以内。 相较于单样本串行处理,并行模式充分释放了 384 核心的处理能力,整机吞吐量提升了一倍。有力地证明了 Sentieon 与第五代 AMD EPYC 处理器的深度协同,能确保在单位时间内完成规模更大的数据周转,显著缩短了大规模样本集的分析周期。 ## 4. 成本优势 我们基于 AWS 预留实例定价及硬件采购成本的初步分析显示,联合方案具有压倒性的成本优势: * AWS EC2 hpc7a.96xlarge 实例的价格大约是同等配置、搭载 AMD 处理器的 PowerEdge 服务器的 4 倍。 * 配备 8x NVIDIA H100 GPU 的 PowerEdge 服务器的价格大约是相同配置但搭载 AMD 处理器的服务器的 5 倍。 * * * # 四、总结 Dell-AMD-Sentieon 联合方案赋予了基因组数据处理卓越的运行速度与扩展灵活性,并实现了性能与成本的最优平衡。不仅解决了“算得慢”的痛点,更通过极高的单机吞吐量降低了总体拥有成本。这不仅是一次算力的升级,更是为精准医疗及大规模人群队列研究量身定制的、可即插即用的工业级生产引擎。 即刻探索搭载 AMD EPYC 处理器的Dell PowerEdge 服务器,若想了解 Sentieon 软件如何加速您的基因组研究。请发送电子邮件至 info@insvast.com 或即刻后台私信以开启 Sentieon 软件的使用。 * * *
chsnp
2026年5月9日 15:51
转发
收藏文档
上一篇
下一篇
手机扫码
复制链接
手机扫一扫转发分享
复制链接
Markdown文件
Word文件
PDF文档
PDF文档(打印)
分享
链接
类型
密码
更新密码
有效期